Wetenschap
Beheersing van gelelektroforese-analyse:een praktische gids
Door John Brennan
Bijgewerkt op 24 maart 2022
Gelelektroforese blijft het werkpaard van laboratoria voor moleculaire biologie. Door een elektrisch veld aan te leggen worden DNA en eiwitten gescheiden – meestal op grootte – in een gelmatrix. Hoewel de techniek gebruikelijk is, varieert de manier waarop de resultaten worden geïnterpreteerd afhankelijk van de downstream-toepassing, of het nu een Western-blot, Northern-blot, Southern-blot of een eenvoudige agarose-run is.
Wanneer u met agarosegels werkt, domineren twee taken:1) het onderscheiden van ongesneden, gekerfde en lineaire plasmiden van uw insert, en 2) het schatten van de fragmentgroottes met behulp van een betrouwbare standaardcurve. De volgende stappen begeleiden u op een duidelijke, reproduceerbare manier door dat proces.
Stap 1 – Identificeer uw rijstroken
Raadpleeg uw laboratoriumnotitieboekje om te bevestigen welk monster in elke baan is geladen. De baanlabels die u bij het laden heeft genoteerd, vormen uw uitgangspunt voor alle daaropvolgende berekeningen.
Stap 2 – Zoek de DNA-ladder
De ladder bevat fragmenten van bekende lengte. De migratieafstanden zullen dienen als referentie voor het dimensioneren van uw onbekende banden.
Stap 3 – Meet de trackingkleurstof
Meet met behulp van een liniaal de afstand van de put tot de trackingkleurstof (de kleurstof die het verst reist). Noteer deze waarde; de eenheden zijn willekeurig zolang ze consistent zijn.
Stap 4 – Bepaal de relatieve mobiliteit
Meet de afstand van elke ladderband tot de put en deel deze vervolgens door de tracking-kleurstofafstand. Dit levert voor elke standaard de relatieve mobiliteit (mobiliteitsfactor) op.
Voorbeeld:als de trackingkleurstof 15 cm aflegde en de ladderbanden 5, 4,5 en 3,5 cm, zijn de relatieve mobiliteiten 0,833, 0,75 en 0,583.
Stap 5 – Registreer mobiliteit en omvang
Voer de relatieve mobiliteiten en bijbehorende fragmentgroottes (in kilobases) in een spreadsheet in. Fabrikanten vermelden deze maten doorgaans in het gegevensblad van de ladder.
Stap 6 – Teken de gegevens
Maak een grafiek met relatieve mobiliteit op de X-as en fragmentgrootte op de Y-as.
Stap 7 – Pas een standaardcurve aan
Gebruik de trendlijnfunctie om een machtswetvergelijking te fitten (bijvoorbeeld y =ax^‑2). Streef naar een R² van minimaal 0,90 om een betrouwbare curve te garanderen.
Stap 8 – Inspecteer de monsterbanden
Kleinere fragmenten migreren verder. Merk op dat supercoiled (ongesneden) plasmiden verder reizen dan lineaire fragmenten van dezelfde grootte, terwijl gekerfde plasmiden langzamer migreren.
Stap 9 – Banden aan samples koppelen
Vergelijk de banden van elke baan met het monster dat u hebt geladen. Voor een plasmide dat is gedigereerd met twee enzymen, zou je twee verschillende banden moeten zien:één aan de bovenkant (insert) en één aan de onderkant (geknipte plasmide). Een digest met één enzym zou een enkele band moeten produceren die iets verder reist dan het ongesneden plasmide, maar veel minder dan het insert.
Stap 10 – Bereken de relatieve mobiliteit van onbekenden
Meet de afstand van de put tot elke onbekende band, deel deze door de tracking-dye-afstand en verkrijg de relatieve mobiliteit.
Stap 11 – Schat de fragmentgrootte
Voer de relatieve mobiliteiten in de vergelijking afgeleid in stap 7 in om de geschatte grootte van elk fragment te berekenen.
Dingen die nodig zijn
- Gegelbeeld met hoge resolutie vastgelegd onder UV-verlichting
- Spreadsheetsoftware (Excel, Google Spreadsheets, enz.)
- Liniaal of schuifmaat voor nauwkeurige afstandsmeting
TL;DR
Als u brede, heldere banden aan de onderkant van elke baan waarneemt, heeft u waarschijnlijk RNA-besmetting. Controleer uw zuiveringsstappen.
 Wat zit er in jouw water? Onderzoekers identificeren nieuwe giftige bijproducten van het desinfecteren van drinkwater
Wat zit er in jouw water? Onderzoekers identificeren nieuwe giftige bijproducten van het desinfecteren van drinkwater  Belangrijkste eigenschappen van natuurlijk versus synthetisch rubber – een technisch overzicht
Belangrijkste eigenschappen van natuurlijk versus synthetisch rubber – een technisch overzicht  Wat zijn de subatomaire deeltjes die de grootste rol spelen bij cellulaire chemische reacties?
Wat zijn de subatomaire deeltjes die de grootste rol spelen bij cellulaire chemische reacties?  Virussen onderscheiden, vernietigen E. coli in drinkwater
Virussen onderscheiden, vernietigen E. coli in drinkwater Er kunnen meer monden worden gevoed door het aantal plantporiën te vergroten
Er kunnen meer monden worden gevoed door het aantal plantporiën te vergroten
 Wat gebeurt er als de luchtdruk en temperatuur dalen?
Wat gebeurt er als de luchtdruk en temperatuur dalen?  Studie voorspelt een aanzienlijk drogere wereld bij 2 C
Studie voorspelt een aanzienlijk drogere wereld bij 2 C Nieuw model beschrijft golfgedrag in zeestraten, voorspelt moordende golven
Nieuw model beschrijft golfgedrag in zeestraten, voorspelt moordende golven Gigantische kelp verandert van dieet wanneer belangrijke voedingsstoffen schaars worden
Gigantische kelp verandert van dieet wanneer belangrijke voedingsstoffen schaars worden Trump aan verkeerde kant van de geschiedenis over klimaat:Ban Ki-moon
Trump aan verkeerde kant van de geschiedenis over klimaat:Ban Ki-moon
Hoofdlijnen
- Wat betekent het voor soorten om een evolutionaire relatie te hebben?
- Wetenschappers ontdekken hoe planten grote wortelziekten bestrijden
- Wat zijn de veranderingen in DNA -sequenties die invloed hebben op genetische informatie die bekend staat als?
- Wat is het verschil tussen erfelijke en milieudefecten?
- Wat zijn biotische beperkende factoren?
- Welke kenmerken moet een hypothese moeten worden beschouwd als wetenschappelijk?
- Hoe wordt polyploïdie gebruikt op het gebied van landbouw?
- Is een Meadow Mouse Carnivore?
- Evolutionaire verbanden tussen prokaryoten en eukaryoten
- Vissers in Istanbul houden traditie in stand ondanks voorraadalarm

- Hoe fruitvliegen hun omgeving opsnuiven

- 2 kiwivogels zijn zeldzaam lichtpuntje in grimmig uitstervingsrapport

- Kan een sluipwesp je fruitgewassen redden?
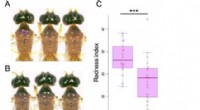
- Teken gedijen goed in warme, vochtige, gastheerrijke omgevingen:klimaatfactoren die hun verspreiding bevorderen

 Wat is de formule voor koper II waterstofsulfaat?
Wat is de formule voor koper II waterstofsulfaat?  Wat is het vierde meest voorkomende mineraal in lichaam?
Wat is het vierde meest voorkomende mineraal in lichaam?  Wordt een wetenschappelijk principe als waar beschouwd?
Wordt een wetenschappelijk principe als waar beschouwd?  Rijkere mensen doen minder in de strijd tegen klimaatverandering
Rijkere mensen doen minder in de strijd tegen klimaatverandering Wat zijn de basiscategorieën van koelmachines?
Wat zijn de basiscategorieën van koelmachines?  Wat is de beste manier om de uitstoot van broeikasgassen te verminderen?
Wat is de beste manier om de uitstoot van broeikasgassen te verminderen? Onderzoekers ontwikkelen een behandelingsaanpak met nanodeeltjes voor een geoptimaliseerde therapie voor alvleesklierkanker
Onderzoekers ontwikkelen een behandelingsaanpak met nanodeeltjes voor een geoptimaliseerde therapie voor alvleesklierkanker  Prooi-foerageren:de collectieve zoektocht of de aanpak van eenzame wolven?
Prooi-foerageren:de collectieve zoektocht of de aanpak van eenzame wolven?
- Elektronica
- Biologie
- Zonsverduistering
- Wiskunde
- French | Italian | Spanish | Portuguese | Swedish | German | Dutch | Danish | Norway |

-
Wetenschap & Ontdekkingen © https://nl.scienceaq.com